2026年3月10日,云南大学生命科学学院彭城团队在国际学术期刊Bioinformatics以Advance Access形式在线接受发表了题为“BrainConnect: processing brain connectivity and spatial transcriptomics data for integrative analysis”的研究论文。该研究开发了一款名为BrainConnect的开源软件,实现了对小鼠单神经元成像、脑连接组、脑空间转录组等多模态数据的整合处理与分析,并基于长短时记忆网络构建了空间基因表达预测大脑区域间连接强度的计算模型,为分析和预测大脑连接组提供计算工具。

大脑神经元之间的复杂连接网络是学习和认知等高等功能的基础之一。目前,通过荧光显微光学切片断层成像(fMOST)可获得单神经元分辨率的连接图像,病毒追踪技术可绘制脑组织的投射组,空间转录组技术则提供了脑组织基因表达数据。然而,这些数据存在着格式不一、缺乏统一分析工具等问题,阻碍了脑连接组和空间转录组的整合研究。
针对上述问题,彭城课题组开发了BrainConnect软件来整合处理异源数据(图1)。该软件使用小鼠大脑通用坐标框架(CCF)将不同格式的单神经元成像、荧光投射与空间转录组数据统一映射到相同脑区体系,整合连接路径与连接强度信息,然后使用长短时记忆网络处理连接路径中的脑区基因表达特征,用于预测起始脑区和终点脑区之间的连接强度。评估表明,该模型预测结果与实验测定连接强度高度正相关,其性能优于其它方法。这也表明融合连接路径信息能有效提升连接强度预测的准确率。该软件还能通过梯度回传方法来筛选预测中具有重要贡献的关键基因,为探索调控大脑连接形成与维持的分子基础提供了线索。
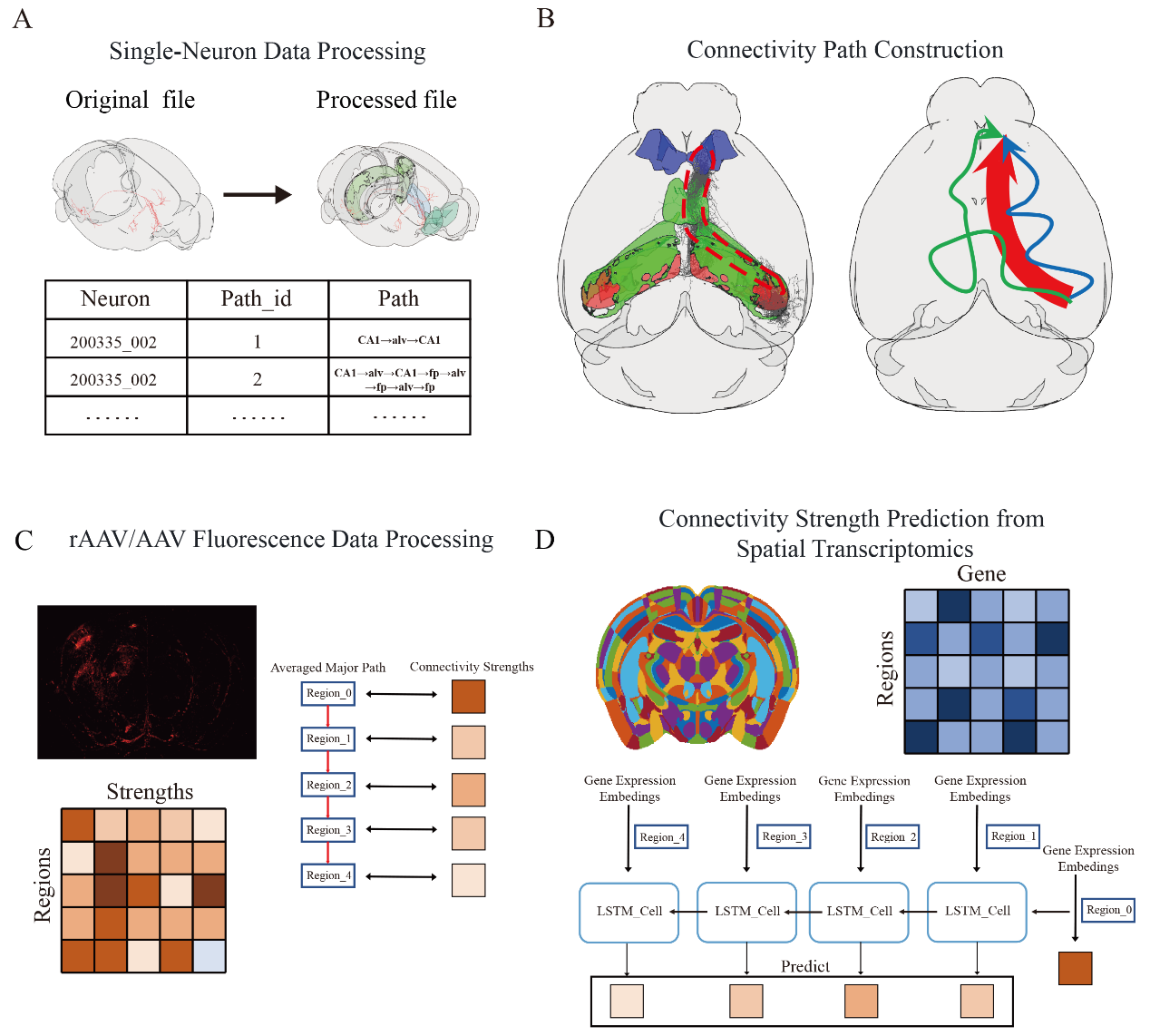
图1.BrainConnect软件功能模块。(A)单神经元数据处理。(B)脑连接路径构建。(C)荧光连接强度数据处理。(D)基于空间转录组的连接强度预测模型。
云南大学生命科学学院彭城研究员为论文通讯作者,硕士研究生桑成龙为第一作者。BrainConnect软件及源代码已在GitHub和PyPI平台开源发布。
论文链接:https://doi.org/10.1093/bioinformatics/btag120
